Эволюционная систематика пытается определить родство и их близость различных организмов. Если не так давно об этом судили по внешним признакам организмов (морфологии если точнее), то теперь однозначно перешли к суждению путем сравнения геномов этих организмов.
Но ДНК в организме занимает большие объемы и сравнить по ней схожесть организмов сильно затруднительно. Кроме того ДНК постоянно эволюционирует. Поэтому биологи начали основываться на рибосомной рибонуклеиновой кислоте (рРНК), т.к. эти молекулы обнаружены у всех клеточных форм жизни, их функции связаны с важнейшим для организма процессом трансляции, первичная структура в целом характеризуется высокой консервативностью.
Считается, что особенностью рРНК является нахождение вне сферы действия отбора, поэтому данные молекулы эволюционируют в результате спонтанных мутаций, происходящих с постоянной скоростью, и накопление таких мутаций зависит только от времени. Таким образом, мерой эволюционного расстояния между организмами служит количество нуклеотидных замен в молекулах сравниваемых рРНК.
Известно, что в рибосомах прокариот и эукариот присутствуют 3 типа рРНК. Информационная емкость крупных молекул больше, но их труднее анализировать. Поэтому наиболее удобным оказался анализ молекул рРНК средней величины: 16S (~1600 нуклеотидов). Систематика основывается на расчете коэффициентов сходства сравниваемых организмов. Именно на основании анализа рРНК современная систематика выделяет три домена бактерии, археи и эукариоты, а так же на этом основывается систематика, бактерий и архей X издания Берги.
Вот такое положение дел в этой сфере на данный момент. Мной же была сделана попытка создать основы для несколько другой, если хотите альтернативной, систематики. Почему? Консервативность рРНК тем не менее не достаточно велика, консервативны лишь некоторые её части. А так как есть достаточно вариабельные части у рРНК, то приходится делать допущения и предполагать, где были разрывы и вставки отдельных фрагментов при мутации. А т.н. выравнивание сейчас делается с очень большой погрешностью.
В итоге, я пришел к выводу, что необходимо при сравнении геномных последовательностей сравнивать такие участки, которые вообще не подвергались мутациям, и которые абсолютно идентичны в разных организмах.
Смотрим, что из этого получилось.
Читать полностью »
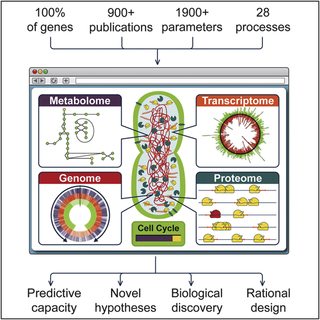 Ученые в Стэнфорде совершили огромный шаг вперед: впервые была создана полная цифровая модель организма и всего его жизненного цикла. Для создания компьютерной модели крошечной бактерии Mycoplasma genitalium потребовалось написать 28 независимых взаимодействующих друг с другом модулей, симулирующих процессы живой клетки и оперирующих 1.900 параметрами. Для описания их поведения использовались 900 различных научных отчетов. Сложность модели высока: лишь для процесса деления одноклеточного требуется 10 часов симуляции, а на выходе получается полгигабайта данных.
Ученые в Стэнфорде совершили огромный шаг вперед: впервые была создана полная цифровая модель организма и всего его жизненного цикла. Для создания компьютерной модели крошечной бактерии Mycoplasma genitalium потребовалось написать 28 независимых взаимодействующих друг с другом модулей, симулирующих процессы живой клетки и оперирующих 1.900 параметрами. Для описания их поведения использовались 900 различных научных отчетов. Сложность модели высока: лишь для процесса деления одноклеточного требуется 10 часов симуляции, а на выходе получается полгигабайта данных.